Relevancia de la formación
Una etapa importante en el desarrollo de la clasificación del orden de las pulgas está asociada con el desarrollo de la investigación genomolecular. En la actualidad, gracias a estos métodos, se confirma el parentesco de las órdenes de pulgas y mecopter. Se están estudiando activamente los genes del ADN ribosómico, factor de elongación de la síntesis de proteínas y del gen mitocondrial citocromo oxidasa II (COII), que se han estudiado en representantes de la mayoría de las familias del orden mecóptero, así como 128 especies de 83 géneros de pulgas de 16 familias (S.G. Medvedev.2009; Whiting 2002; Whiting et al.2008). La filogenia de las pulgas se reconstruye sobre la base de los datos de estos genes mediante diversos métodos de construcción de árboles filogenéticos y modelos para calcular distancias por pares, que a menudo se presenta en forma de árbol de consenso (consenso strick) (Whiting et al. 2008). Sin embargo, en algunos casos, los resultados de los estudios genomoleculares contradicen el esquema de los lazos familiares,obtenido sobre la base de análisis filogenético. Además, de acuerdo con diferentes interpretaciones de los datos genéticos moleculares, el origen de los infraórdenes clave de las pulgas se puede interpretar de diferentes maneras. Entonces, desde el punto de vista de diferentes autores, los mismos clados de pulgas pueden ser grupos polifiléticos y monofiléticos (Whiting et al.2008, S.G. Medvedev.2019). Esto puede estar relacionado tanto con las peculiaridades de la ecología de la fauna de pulgas moderna como con varios problemas metodológicos del trabajo con datos genéticos moleculares.y grupos monofiléticos (Whiting et al. 2008, S.G. Medvedev. 2019). Esto puede estar relacionado tanto con las peculiaridades de la ecología de la fauna de pulgas moderna como con varios problemas metodológicos del trabajo con datos genéticos moleculares.y grupos monofiléticos (Whiting et al. 2008, S.G. Medvedev. 2019). Esto puede deberse tanto a las peculiaridades de la ecología de la fauna de pulgas moderna como a varios problemas metodológicos de trabajar con datos genéticos moleculares.
Con respecto al primer punto, debe enfatizarse que el aislamiento de líneas filéticas separadas de pulgas, que tienen un estatus igual en taxonomía, ocurrió en diferentes intervalos históricos. Esto, a su vez, significa que la fauna de pulgas son fragmentos dispersos de una extensa paleofauna, que ahora está en gran parte extinta (S.G. Medvedev.2009, S.G. Medvedev.2019). De esto se desprende que con diferentes enfoques metodológicos de los estudios genéticos moleculares, podemos perder de vista la evolución convergente de secuencias de nucleótidos (homoplasia), lo que puede conducir a errores en la determinación de la topología del árbol y a un bajo soporte estadístico de ramas. Entonces, por ejemplo, usando datos que tienen diferentes relaciones para diferentes taxones y, en consecuencia, diferentes relaciones con diferentes partes de genes,encontraremos lagunas en las secuencias y la ausencia de datos para diferentes loci para diferentes muestras (S.G. Medvedev.2019, Lukashov V.V.2006). Por lo tanto, a la hora de elegir un método de investigación, se deben tener en cuenta todos estos problemas y se deben seleccionar muestras de los taxones de pulgas más estudiados y comunes para luego compararlos con las muestras de mecópteros más estudiados. De esta manera podemos construir un árbol más confiable con un alto soporte.
, Siphonaptera Mecoptera -II (COII).
:
Siphonaptera NCBI [5], .
(COX 1) Siphonaptera .
-II (COII) Mecoptera Siphonaptera NCBI [1].
MEGA X.
.
NCBI [5] : Chaetopsylla globiceps (Taschenberg, 1880), Chaetopsylla trichosa (Kohaut, 1903), Ctenocephalides felis (Bouché, 1835), Ctenocephalides canis (Curtis, 1826), Ceratophyllus sciurorum (Schrank, 1803), Leptopsylla segnis (Schönherr, 1811). , NCBI[1], Boreus: Boreus westwoodi (Hagen, 1866), Boreus hymalis (Linnaeus, 1767), Boreus coloradensis (Byers, 1955), Boreus nivoriundus (Fitch, 1847), Boreus brumalis (Fitch, 1847), Boreus californicus (Packard, 1870), (.1.).
UPGMA [2] , - 500 [3]. Muscle (. 2.) MEGA X [4]. Muscle . , . translate DNA to protein and vice versa (.3), . (. 3.) , - , . (.4). MEGA . Modeltest 3.06 PPC (Posada, D., Crandall, K.C., 1999) (AIC), . AIC , , (Posada, D., Buckley, T.R., 2004.). MEGA X [4] 64- Windows 10 Home 4- INTEL 1,6 1 .
- [6] (.5.). 12 . 1-+2-+3-+. ( ). 742 .
( 1.)

(.2.)
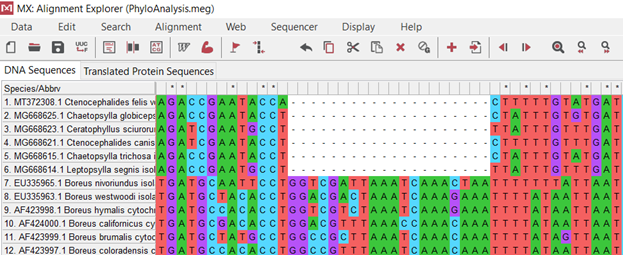
(.3.)
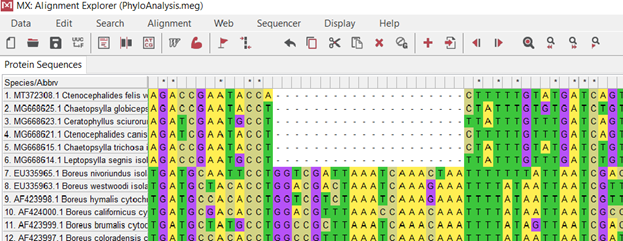
(.4.)
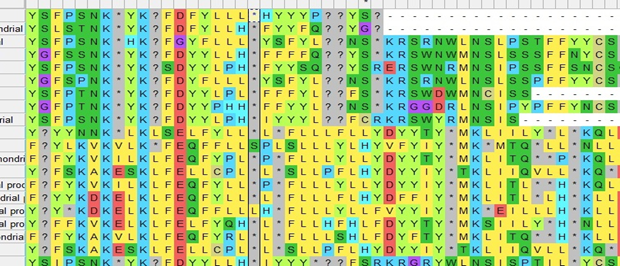
(.5)
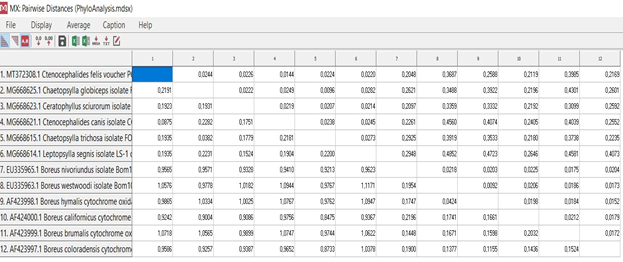
. Mecoptera Siphonaptera. 60% , Mecoptera Siphonaptera. , , , .
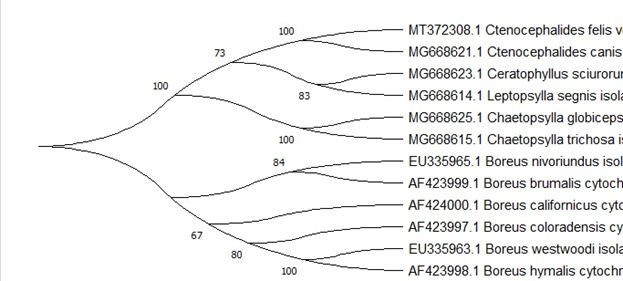
, MEGA X [4] (80%-100%) , . Ceratophyllus sciurorum Leptopsylla segnis (73%), . , (.. .2009; Whiting 2002; Whiting et al. 2008).
Mecoptera Siphonaptera . . Boreus nivoriundus Boreus brumalis (80%) «» Chaetopsylla globiceps Chaetopsylla trichosa (100%). , Mecoptera Siphonaptera. Boreus californicus (67%) . , . (.6.)
(.6.)
. . , , , . . . . [https://vk.com/phanerozoi] . , .
.
, , .
, .
1. Whiting M.F. 2002. Mecoptera is paraphyletic: multiple genes and phylogeny of Mecoptera and Siphonaptera. Zoologica Scripta, 31: 93–104
2. Whiting M.F., Whiting A.S., Hastriter M.W. and Dittmar K. 2008. A molecular phylogeny of fleas (Insecta: Siphonaptera) and host associations. Cladistics, 24: 1–31.
3. , .. , 313, № 3, 2009, c. 273–282
4. (SIPHONAPTERA) .., .. III , 2009, . 185-190
5. / .. —.. , 2009. — .256. .29-31.
6. Posada, D., Buckley, T.R., 2004. Model selection and model averaging in phylogenetics: advantages of the AIC and Bayesian approaches over likelihood ratio tests. Syst. Biol. 53, 793–808.
7. Posada, D., Crandall, K.C., 1999. Modeltest. Bioinformatics 14, 817–818.
1. http://lifemap.univ-lyon1.fr
2. Sneath P.H.A. and Sokal R.R. (1973). Numerical Taxonomy. Freeman, San Francisco.
3. Felsenstein J. (1985). Confidence limits on phylogenies: An approach using the bootstrap. Evolution 39:783-791
4. Kumar S., Stecher G., Li M., Knyaz C. y Tamura K. ( 2018 ). MEGA X: Análisis de genética evolutiva molecular en plataformas informáticas. Biología Molecular y Evolución 35 : 1547-1549.
5.https: //www.ncbi.nlm.nih.gov/pmc/articles/PMC4681159/
6. Tajima F. y Nei M. ( 1984 ). Estimación de la distancia evolutiva entre secuencias de nucleótidos. Biología molecular y evolución 1 : 269-285.